关于Cytoscape利用蛋白质互作网络分析info文件绘制网络图过程中节点String_id转换成GeneID 或者Symbol问题
有学员反映在学习GEO芯片数据挖掘,进行利用差异基因进行蛋白质互作网络分析的过程中,获得的info文件中之涉及了String_id,利用Cytoscape进行绘图的过程中无法知道对应的具体基因ID是什么...
有学员反映在学习GEO芯片数据挖掘,利用差异基因进行蛋白质互作网络分析的过程中,获得的info文件中之涉及了String_id,利用Cytoscape进行绘图的过程中无法知道对应的具体基因ID是什么或者Gene Symbol是什么,这些并不能直观显示。可以通过以下方法进行解决:
1、输入文件为差异表达分析的结果文件,文件中第一列是基因ID,有时会添加第二列Gene Symbol作为补充信息,其他为差异分析的结果文件。
2、基于差异表达文件中的Gene ID与String数据库对应数据比对,可以获得能够比对上的蛋白String_id。此时获得的变量deg_mapped中其实包括了很的信息,包括差异表达文件中的信息,和比对上的String_id信息,可以将该向量的所有信息利用write.table()保存成文本文件,并进行整理,使其包含GeneID、GeneSymbol 以及String_id(也可包含其他数据),后期作为table导入Cytoscape,方便修改节点label。
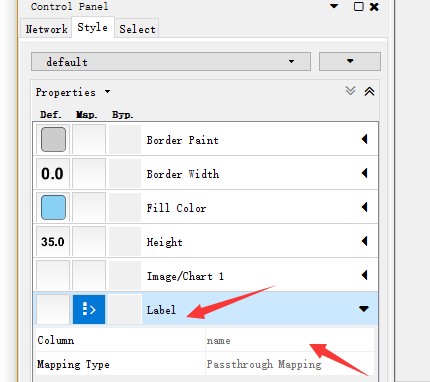
3、获得的Info文件,根据cytoscape使用方法导入,开始构建网络图,在进行点线设置的过程中,将整理后的deg_mapped对应的文件,作为Table导入,File——Import——Table——File,设定识别节点为String_id。之后在控制面板,Style下,修改节点Node的label显示,设置显示为输入table的Gene或者Symbol列即可让图片上节点显示的标签发生改变。
(部分细节见下图)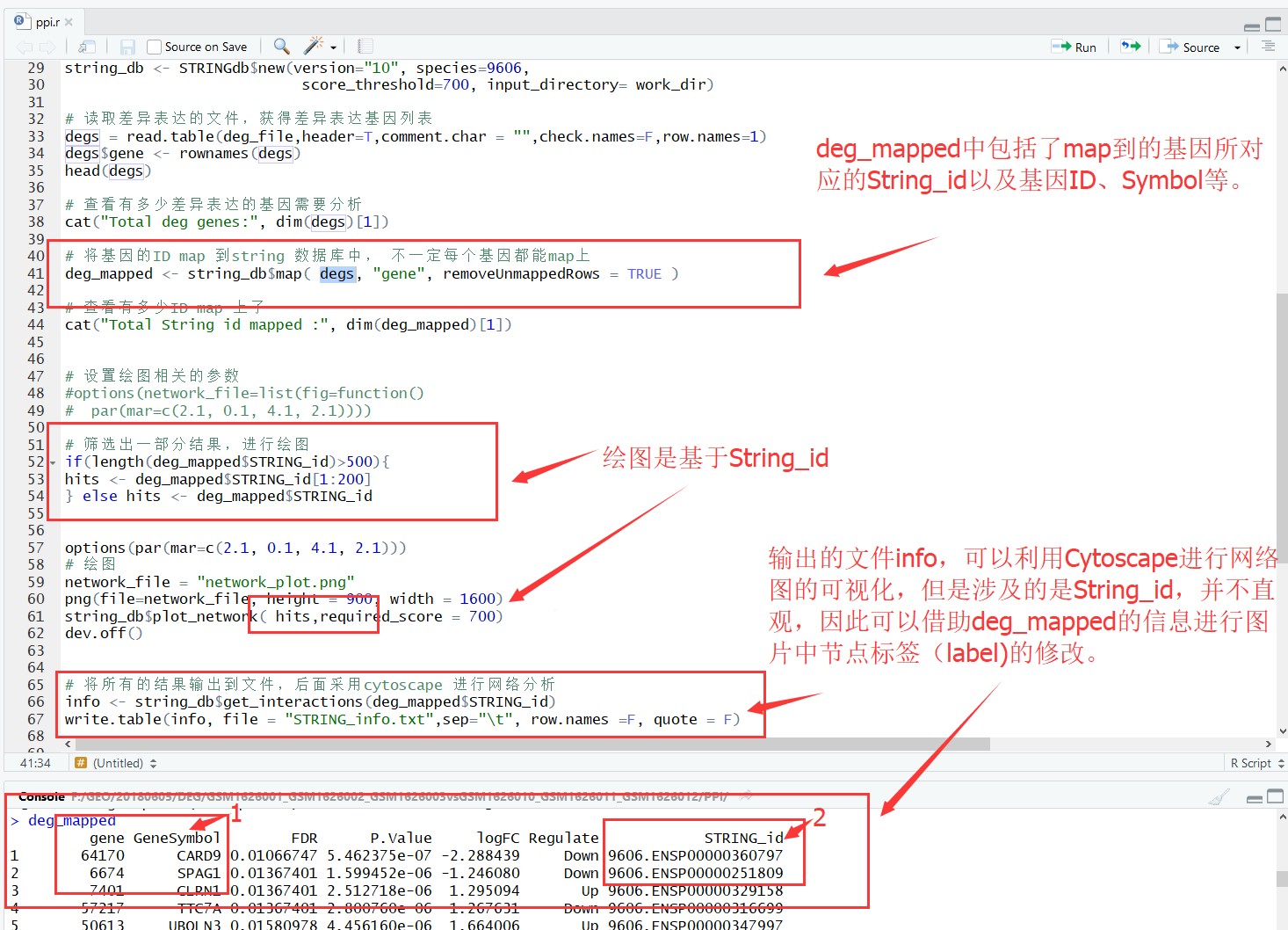
相关课程推荐:GEO芯片数据挖掘、GEO芯片数据标准化、Cytoscape与网络图绘制课程
更多生物信息课程:
1. 文章越来越难发?是你没发现新思路,基因家族分析发2-4分文章简单快速,学习链接:基因家族分析实操课程、基因家族文献思路解读
2. 转录组数据理解不深入?图表看不懂?点击链接学习深入解读数据结果文件,学习链接:转录组(有参)结果解读;转录组(无参)结果解读
3. 转录组数据深入挖掘技能-WGCNA,提升你的文章档次,学习链接:WGCNA-加权基因共表达网络分析
4. 转录组数据怎么挖掘?学习链接:转录组标准分析后的数据挖掘、转录组文献解读
5. 微生物16S/ITS/18S分析原理及结果解读、OTU网络图绘制、cytoscape与网络图绘制课程
6. 生物信息入门到精通必修基础课:linux系统使用、perl入门到精通、perl语言高级、R语言入门、R语言画图
7. 医学相关数据挖掘课程,不用做实验也能发文章:TCGA-差异基因分析、GEO芯片数据挖掘、GEO芯片数据标准化、GSEA富集分析课程、TCGA临床数据生存分析、TCGA-转录因子分析、TCGA-ceRNA调控网络分析
8.其他,二代测序转录组数据自主分析、NCBI数据上传、二代测序数据解读
- 发表于 2018-07-16 10:26
- 阅读 ( 9019 )
- 分类:视频课程
你可能感兴趣的文章
- cytoscape软件的安装与使用_v3.10.2 4837 浏览
- cytoscape-cytoHubba插件的安装与使用 21945 浏览
- cytoscape软件安装与使用-绘制蛋白互作网络图 7798 浏览
- Cytoscape如何基于点的属性快速对点和相连的线进行颜色分类 17142 浏览
- 网络概念以及Cytoscape导入数据格式理解(ceRNA等多元关系网络数据) 12151 浏览
- cytoscape插件BinGO安装以及GO富集分析和网络可视化 292127 浏览
0 条评论
请先 登录 后评论
