如何利用NCBI提取特定位置的基因组序列?
小编经常遇到这样的一些个性化分析,例如,下载某物种某染色体XXXX-XXXX碱基区域内的全部基因信息,尤其是BSA、QTL定位、GWAS等项目客户,该类需求是很多的;之前给大家分享过一个利用Ensembl数...
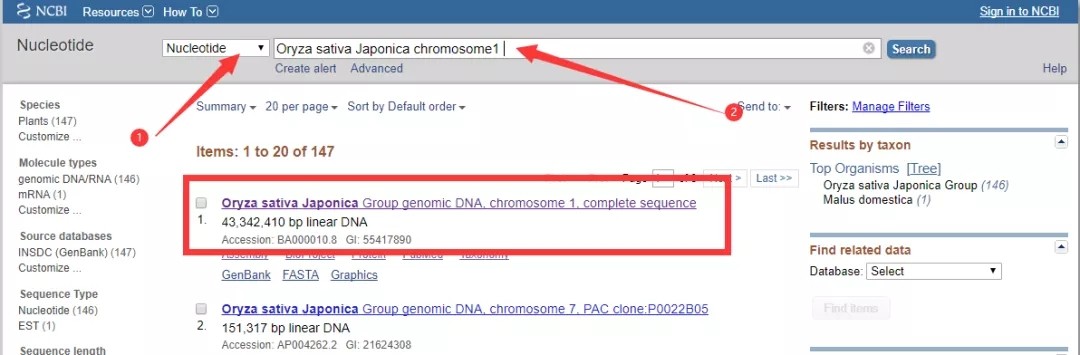
小编经常遇到这样的一些个性化分析,例如,下载某物种某染色体XXXX-XXXX碱基区域内的全部基因信息,尤其是BSA、QTL定位、GWAS等项目客户,该类需求是很多的;之前给大家分享过一个利用Ensembl数据库网站提供的biomart工具进行基因组特定区间基因及注释信息的提取,详见链接:[原创]-如何下载特定区间内基因及注释信息?但由于ensembl收录基因组数量有限,对于未收录物种就只能另寻他法了。今天我再给大家演示一个利用NCBI数据库进行基因组特定序列提取的方法,希望对您的科研学习有所帮助。我们以水稻(日本晴)1号染色体正义链1234-4321位置序列为例进行介绍。1. 打开NCBI,类目选择Nucleotide,检索框输入日本晴拉丁名及染色体号(Oryza sativa Japonica chromosome1 ),点search检索到日本晴1号染色体序列,如下图:
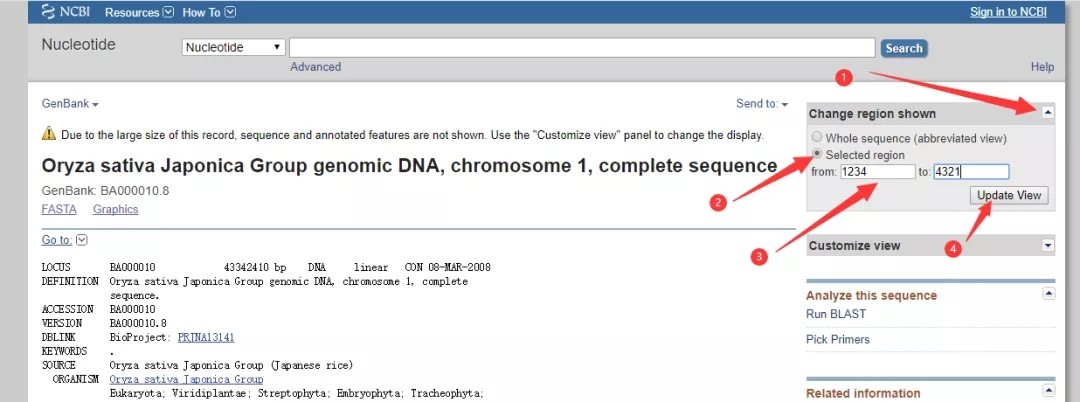
2. 点击上图检索到的日本晴1号染色体序列进入下一步,如下图,在页面右侧有Change region shown选项,展开后选择Selected region 并输入1234-4321位置信息,点击Update view进入下一步。
 3. 点击页面左上角gene bank,格式更改为 FASTA,然后页面就自动展示该区域序列信息了。
3. 点击页面左上角gene bank,格式更改为 FASTA,然后页面就自动展示该区域序列信息了。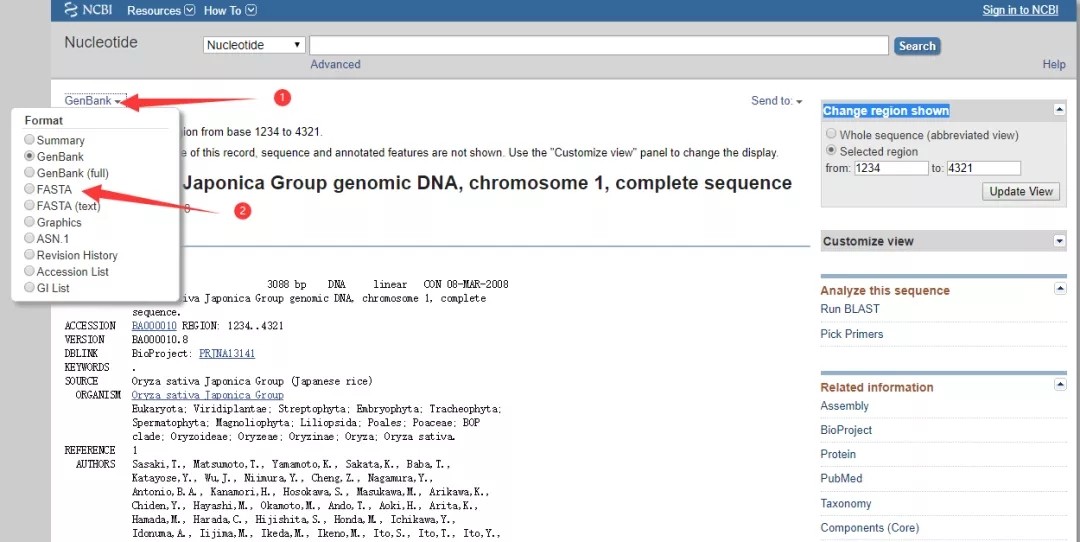 4. 假如想知道该区域的反义链序列则可进行下方操作:在步骤3的基础上,点击页面右侧的Customize view选项,勾选Show reverse complement即可。
4. 假如想知道该区域的反义链序列则可进行下方操作:在步骤3的基础上,点击页面右侧的Customize view选项,勾选Show reverse complement即可。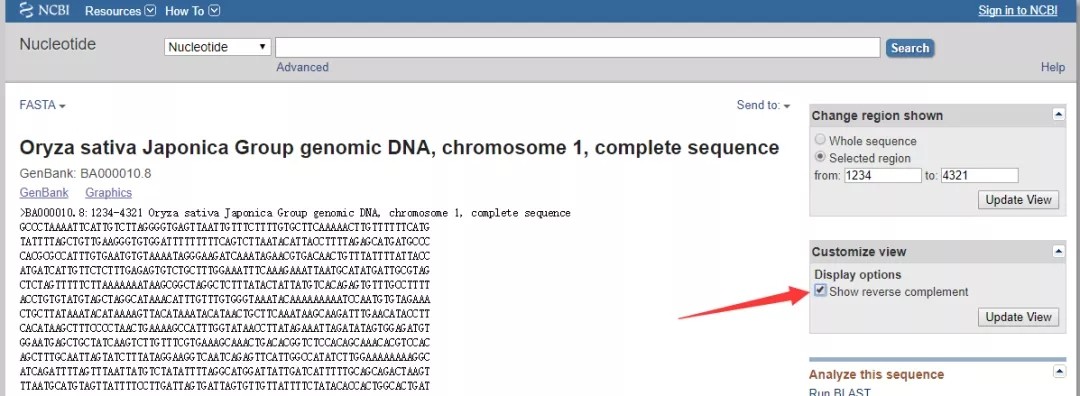 好了,今天的生信小技能就介绍到这里,更多生信小技能大家可以学习一下下方小课程:《转录组标准分析后的数据挖掘》:无需编程8种常用生信小技能,简单易学;限时7.7折优惠,活动截止2020年3月19日。
好了,今天的生信小技能就介绍到这里,更多生信小技能大家可以学习一下下方小课程:《转录组标准分析后的数据挖掘》:无需编程8种常用生信小技能,简单易学;限时7.7折优惠,活动截止2020年3月19日。 需要的可以扫描下方二维码查看学习:
需要的可以扫描下方二维码查看学习:
- 发表于 2020-03-17 14:20
- 阅读 ( 6763 )
- 分类:基因组学
你可能感兴趣的文章
相关问题
0 条评论
请先 登录 后评论
