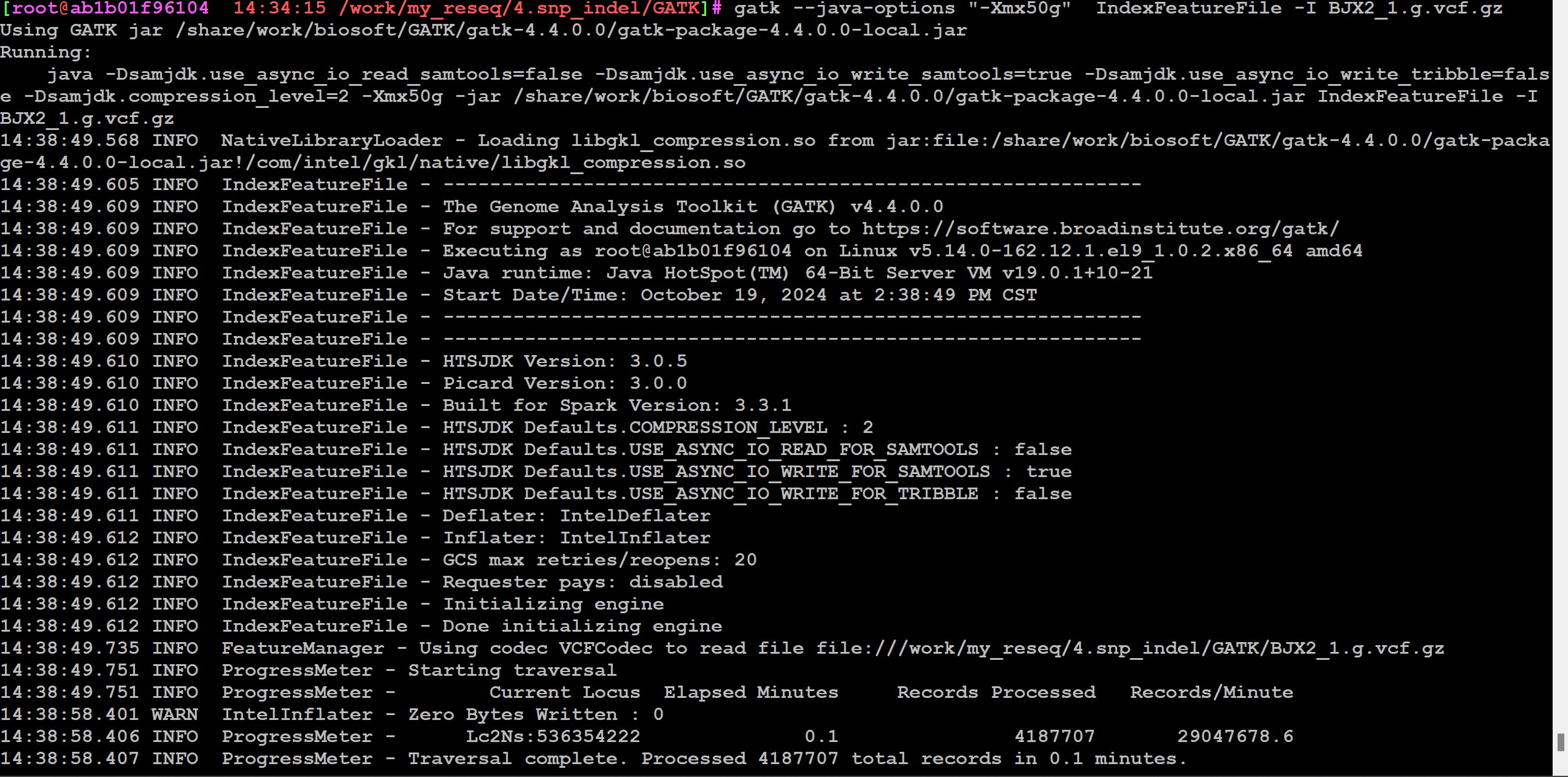
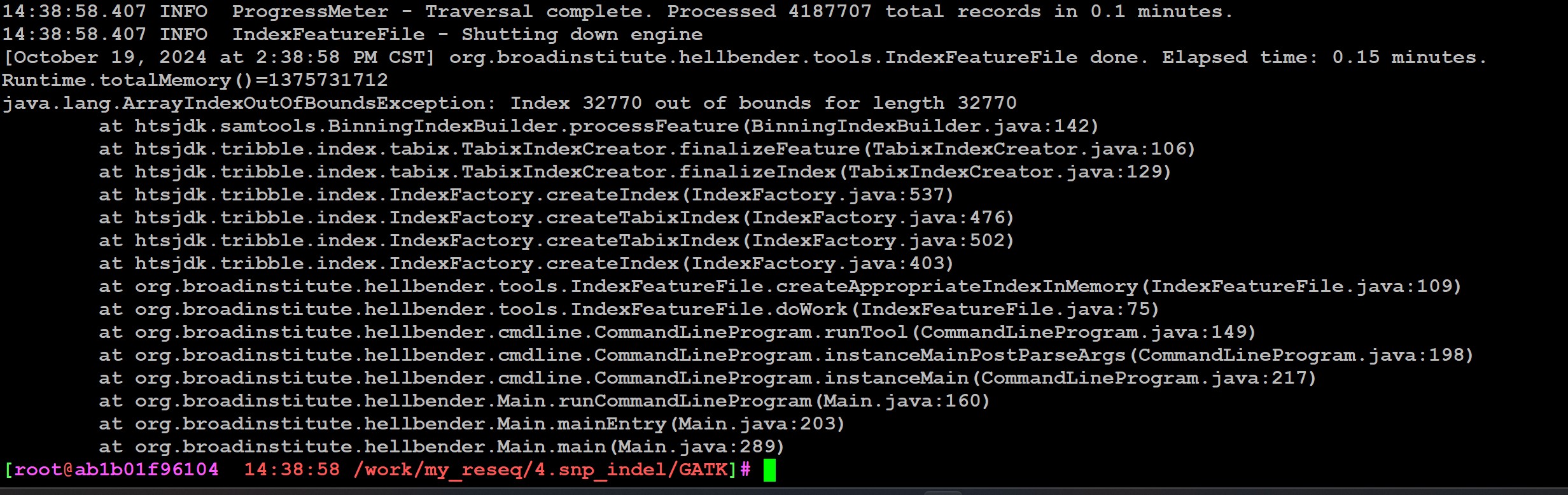
如果你的样品少,可以用gatk直接生成vcf文件,就不要生成gvcf了
1 个回答
- 1 关注
- 0 收藏,756 浏览
- 啊呀。 提出于 2024-10-19 14:48
相似问题
- 合并GVCF文件 1 回答
- gatk无法利用csi索引 0 回答
- 老师们好,在生成gvcf文件合并vcf文件时,出现这种警告信息,请问是什么原因,如何处理啊? 1 回答
- 老师,在生成gbcf文件后,发现只运行了前三个染色体的,是我的代码有问题嘛?该怎么解决啊?参考基因组的fasta,fai文件都是好的,前期生成的bam文件也是好的,样品是四倍体,参考基因组是异源四倍体 1 回答
- 老师,我的db文件夹里显示了所有染色体都已经导入,但是在将gvcf转换成vcf时,发现在Lc2Ns染色体就结束完成了,这是正常现象嘛,是我使用的近源种参考基因组的原因嘛?我的是简化基因组测序的 1 回答
- 老师,问题比较复杂,麻烦您看一下详细的问题描述,小麦基因组 2 回答